Seltene Tumore besser erkennen
-
 <ic:message key='Bild vergrößern' />
<ic:message key='Bild vergrößern' />
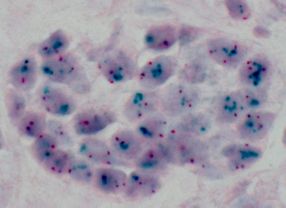
- Eine Probe mit Tumorgewebe, das durch die CISH-Methode angefärbt wurde. Jeder dunkle Punkt kennzeichnet eine Stelle in den Tumorzellen, an denen ein Tumorgen mit den DNA-Sonden reagiert hat. Quelle: Institut für Pahtologie der Universität Erlangen-Nürnberg
12.01.2010 -
Krebs kann sich in jeder Stelle des Körpers bilden. Selbst in Muskeln, Fett- und Nervengewebe können Tumoren entstehen. Solche Weichteiltumoren oder Sarkome zählen jedoch zu den seltenen Krebserkrankungen und werden deshalb oft nur schwer erkannt. An einer verbesserten Diagnostik arbeiten jetzt Forscher des Universitätsklinikums Erlangen und der Friedrich-Schiiller-Universität Jena mit zwei Unternehmen aus Bremerhaven und Berlin zusammen. Das Projekt, das klassische Anfärbetechniken mit DNA-Chips kombiniert, wird vom Bundesministerium für Bildung und Forschung innerhalb der Initiative "KMU innovativ" gefördert.
Rund 4.000 Menschen in Deutschland erkranken jährlich an bösartigen Weichteiltumoren. Die sogenannten Sarkome betreffen das Bindegewebe, aber auch Knochen, Knorpel, Muskeln und das Fettgewebe. Sarkome sind zwar relativ selten - nur etwa jede hundertste Krebserkrankung gehört dazu - aber ebenso gefährlich. Noch dazu sind die etwa hundert verschiedenen Sarkom-Varianten für Ärzte nur schwer zu erkennen. Meist gelingt das nur in einem sehr späten Stadium der Erkrankung. Eine frühe Diagnose würde die Überlebenschancen vieler Patienten verbessern.
| KMU-innovativ |
Im Jahr 2007 erweiterte das BMBF die erfolgreichen Förderinitiativen BioChance und BioChancePlus. Unter dem Titel "KMU-innovativ" werden nun kleine und mittlere Unternehmen unterstützt, die besonders aufwendige Forschungen betreiben. Insgesamt 300 Millionen Euro stehen bis zum Jahr 2015 für zunächst fünf Technologiefelder zur Verfügung Mehr Informationen zur Förderinitiative auf biotechnologie.de: hier klicken |
Jeden Tumor individuell bewerten
Einen Weg könnte die Biotechnologie aufzeigen. Denn bei vielen Sarkomen sind in den Tumorzellen genetische Veränderungen zu finden. Diese charakteristischen Abweichungen im Erbgut könnten dazu dienen, abnormale Zellen nicht nur schnell ausfindig zu machen, sondern sie auch eindeutig zu identifizieren. Neben einer generell besseren Diagnostik für Weichteiltumoren könnte damit der Tumor jedes Patienten individuell bewertet und die Therapie entsprechend genau darauf abgestimmt werden. Ein einfaches Instrument zum Erkennen dieser genetischen Veränderungen zu entwickeln, das ist das Ziel eines Verbunds, in dem Forscher des Universitätsklinikums Erlangen und der Friedrich-Schiller-Universität Jena mit ihren Kollegen der Berliner Chipron GmbH und der ZytoVision GmbH aus Bremerhaven zusammenarbeiten. Beide Unternehmen werden über die Initiative KMU innovativ unterstützt, in der die Firmen jeweils die Hälfte der Projektkosten selbst aufbringen, die andere Hälfte in Höhe von 412.000 Euro wird vom BMBF übernommen. Am Ende soll ein Nachweis stehen, der zwei verschiedene Methoden kombiniert und damit zwölf spezifische Veränderungen bei insgesamt zehn Weichteiltumoren nachweisen soll.
| Mehr zum Thema auf biotechnologie.de |
News: Gezielte Suche nach Erbgutfehlern in Krebszellen News: Nationale Krebsinitiative - Vom Labor ans Krankenbett Menschen: Frank Bier - Labor im Zwergenmaßstab |
Die Wissenschaftler in der Pathologie liefern dazu die diagnostische Expertise und erstellen sogenannte Gewebe-Chips, während die Firmen ihr Knowhow einerseits in Form von speziell markierten DNA-Sonden zur sogenannten chromogenen in-situ Hybridisierung (CISH) und andererseits über DNA-Chips (sogenannte LCD Arrays) zur Verfügung stellen. Das Pathologische Institut in Erlangen hat bereits in zahlreichen Studien an der Entwicklung neuer DNA-Sonden in der Molekularen Pathologie mitgewirkt. Die Pathologie in Jena verfügt über eine Gewebebank von mehreren tausend Tumorproben, da sie seit langem das Referenzzentrum für Sarkomdiagnostik in Deutschland ist. Diese Fälle sollen jetzt in ein sogenanntes Gewebs-Mikroarray gebracht werden. In einem nur zwei Zentimeter großen Paraffinblock haben so bis zu 1.000 Sarkome von unterschiedlichen Patienten Platz und können mit den neuen Techniken automatisiert analysiert werden. Damit, so hoffen die Forscher, lassen sich schnell die entsprechenden charakteristischen Genveränderungen finden, die bei den verschiedenen Tumorarten auftreten.
Kombination aus Farbnachweis und DNA-Chip
Typisch für genetische Veränderungen, die bei Weichteiltumoren häufig auftreten, ist der Austausch von Genabschnitten unterschiedlicher Chromosomen. Diese so genannten chromosomalen Translokationen wollen die beteiligten Firmen auf zweierlei Art als Biomarker verwenden. Die erste Methode dazu ist das Anfärben der Gene. Sind die Tumorgene erst einmal bekannt, fertigen die Forscher entsprechende Gegenstücke aus DNA an, die auf das Tumorerbgut wie der Schlüssel zum Schloss passt. In diesem Fall wird ein mit der DNA-Sonde verbundener Farbstoff aktiviert. Der Forschungsverbund nutzt dazu die sogenannte chromogene In-situ-Hybridisierung (CISH), bei der das entstehende Farbsignal mit einem einfachen Lichtmikroskop zu erkennen ist. Bei dem bisher standardmäßig verwendeten Verfahren, der Fluoreszenz-in-situ-Hybridisierung (FISH), ist dagegen ein komplizierteres Fluoreszenzmikroskop notwendig, um die Verfärbungen zu erkennen.
Bei der zweiten Methode werden die Tumorgene über DNA-Chips erkannt. Auf dem Chip befinden sich dicht nebeneinander gepackt eine Reihe von DNA-Stücken mit jeweils einem unterschiedliches Tumorgen. Die Gewebeprobe eines Patienten, die zuvor mit einem Farbstoff versehen wurde, wird über den Chip gegossen. Passen die Stücke in der Probe und auf dem Chip zusammen, befinden sich also Tumorgene im Erbgut des Patienten, dann leuchtet die Stelle auf dem Chip auf, wo sich das entsprechende DNA-Bruchstück befindet. Im Vergleich zu CISH oder FISH sind mit einem DNA-Chip nicht nur qualitative Aussagen möglich (Ist ein Tumorgen vorhanden?), sondern auch quantitative (Wie stark ist es aktiv?).
Beide Techniken zusammen, so erhoffen sich die Forscher, werden die Diagnose von Sarkomen entscheidend verbessern. "Ich erwarte, dass am Ende des Projekts Produkte vorliegen, die auch in der täglichen Routinediagnostik in der Pathologie eingesetzt werden", sagt Arndt Hartmann vom Universitätsklinikum Erlangen. Um diese ehrgeizigen Ziele zu erreichen, haben die Forscher noch Zeit bis zum Frühjahr 2012. Dann endet die Förderugn des BMBF.