Leukämie: Spurensuche in der Genom-Verpackung
-
 <ic:message key='Bild vergrößern' />
<ic:message key='Bild vergrößern' />
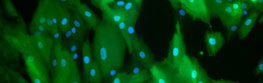
- Epigenetische Forschungen sollen helfen, Krankheiten wie CLL besser zu verstehen. Quelle: Daniel Mertens
25.04.2012 -
Die chronische lymphatische Leukämie (CLL) ist die häufigste Leukämie bei Erwachsenen. Dabei entarten die weißen Blutkörperchen, sie verlieren die Fähigkeit, ihren natürlichen Zelltod auszulösen. Zwar ist die Erkrankung recht gut behandelbar, allerdings sprechen etwa zehn Prozent der Patienten nicht auf die Therapie an. Ein Grund könnte im epigenetischen Code der entarteten Zellen liegen. Darum will ein Forscherkonsortium des Deutschen Krebsforschungszentrums (DKFZ) in Heidelberg, der Universitätsklinik Ulm und des Berliner Max-Planck-Instituts für molekulare Genetik Veränderungen bei den chemischen Anhängseln der Erbsubstanz bei CLL untersuchen. Die Suche nach den Abweichungen in der Verpackung der DNA, die mit der Erkrankung zusammenhängen, fördert das Bundesforschungsministerium mit drei Millionen Euro.
Die Gründe, warum ein Gen defekt ist oder normal funktioniert, liegen nicht nur in der Sequenz der DNA selbst. Die Verpackung gibt mit den Ausschlag – auch die Moleküle, die an die DNA binden, haben einen Einfluss darauf, ob ein Gen an- oder abgeschaltet wird und die Zelle ganz nach Plan ihre Funktion ausübt oder davon abweicht. Bei der Zellteilung werden nicht nur die DNA, sondern auch diese epigenetischen Faktoren an die Tochterzellen weitergegeben. Die Epigenetik gerät deshalb mehr und mehr in den Fokus der Krebsforschung; neben einem millionenschweren Forschungsprogramm der Europäischen Union lässt sich auch das BMBF die Forschung am Epigenom einiges kosten (mehr...).In dieser Folge der Kreidezeit erklären wir, was sich hinter dem Begriff Epigenetik verbirgt.Quelle: biotechnologie.tv
So auch im Zusammenhang mit der chronischen lymphatischen Leukämie, der CLL. „Inzwischen wissen wir ziemlich genau, welche Defekte es bei der CLL im Genom gibt“, erläutert Daniel Mertens vom Universitätsklinikum Ulm. Es gäbe jedoch viele Anhaltspunkte, dass auch epigenetische Faktoren eine entscheidende Rolle bei der CLL spielen. „Bei Mäusen mit einer ähnlichen Erkrankung haben wir beispielsweise gesehen, dass die epigenetischen Veränderungen zuerst da waren und erst später Defekte in der DNA auftraten.“
Programmierter Zelltod ausgeschaltet
Ein Gen, das durch die epigenetische Verpackung inaktiviert wird, ist DAPK1. Normalerweise trägt es nach etwa vier Tagen Lebenszeit zum natürlichen Zelltod jener Immunzellen, die B-Lymphozyten genannt werden. Bei allen CLL-Patienten ist das DAPK1-Gen jedoch epigenetisch verändert und verhindert, dass die Zellen sterben. Diese sammeln sich dann in den Lymphknoten und im Knochenmark an und verdrängen dabei andere Zelltypen des blutbildenden Systems.
Daniel Mertens leitet gemeinsam mit Karsten Rippe vom Deutschen Krebsforschungszentrum in Heidelberg das vom BMBF geförderte Forschungsnetzwerk „CancerEpiSys“. Über einen Zeitraum von drei Jahren werden sie mit ihren Arbeitsgruppen die epigenetischen Defekte der CLL untersuchen. Unter anderem wollen die Forscher im Reagenzglas B-Lymphozyten mit Substanzen versetzen, von denen bekannt ist, dass sie die Epigenetik beeinflussen. Diese Veränderungen wollen sie Schritt für Schritt aufzeichnen und auf dieser Grundlage ein Analyseschema entwickeln, das Aussagen über die Entwicklung der CLL und den spezifischen Krankheitsverlauf beim Patienten ermöglicht.
| Mehr zum Thema auf biotechnologie.de |
News: Millionenschweres Epigenom-Projekt startet News: Genetischer Steckbrief für Leukämiezellen Wochenrückblick: Epigenetik verrät Erfolgschancen der Chemotherapie |
Eine Menge akribischer Fleißarbeit steht den Wissenschaftlern bevor. Sie wollen sich so viele Patientenproben wie möglich genau anschauen und deren Epigenetik beschreiben, das heißt, wie in den Zellen die DNA verpackt ist und wie sie durch zelluläre Prozesse verändert werden. In einem weiteren Arbeitspaket sollen einzelne Zellen mit Fluoreszenzfarbstoffen angefärbt und unter speziellen Mikroskopen betrachtet werden. Beides soll Aufschluss darüber geben, wie heterogen der Tumor ist, welche Gene in der CLL jeweils durch epigenetische Faktoren verändert werden und wie sich das auf den individuellen Krankheitsverlauf beim Patienten auswirkt. Ein drittes Arbeitspaket widmet sich der Frage, wie sich die Epigenetik und auch das Genom selbst verändert, wenn den Zellen bestimmte, die Epigenetik beeinflussende Substanzen hinzugefügt werden.
Menschen und Maschinen
Mit Hilfe von Hochleistungsrechnern sollen all diese Daten ausgewertet werden. In silico sollen so Zusammenhänge hergestellt und Modelle entwickelt werden, die erklären können, was genau in den Zellen passiert und welchen Verlauf die Leukämie nehmen wird. Eine Besonderheit an dem Forschungsnetzwerk sei, dass die Experimente auf der einen und die Auswertung per Computer auf der anderen Seite sich die Waage halten, betont Mertens. „Die Informatik spielt in der Molekularbiologie ja eine immer wichtigere Rolle und macht mittlerweile oft den größeren Anteil der Forschungsaktivitäten aus“, so der Biochemiker.
Bei CancerEpiSys geht es allein um die Grundlagenforschung und darum, die Epigenetik der CLL zu verstehen. Alternative Therapieformen, von denen vor allem die Patienten profitieren könnten, die auf die derzeitigen Behandlungen nicht ansprechen, sollen aber in einem weiteren Forschungsprojekt entwickelt werden. Dazu arbeiten das Deutsche Krebsforschungszentrum, das Universitätsklinikum Ulm und andere Forschungseinrichtungen in einem virtuellen Institut der Helmholtz-Gemeinschaft zusammen.
Autorin: Anke Wilde