Die virtuelle Welt der Biologen
-
 <ic:message key='Bild vergrößern' />
<ic:message key='Bild vergrößern' />
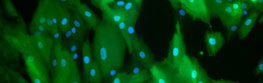
- Die Systembiologie ist ein interdisziplinärer Forschungszweig, bei dem Mathematiker und Informatiker gemeinsam mit Biologen virtuelle Modelle komplexer biologischer Prozesse am Computer simulieren. Quelle: BMBF
26.04.2007 -
Um biologische Vorgänge besser zu verstehen, kommen zunehmend Mathematiker und Informatiker zum Einsatz. Mit ihrer Hilfe wollen Biologen virtuelle Modelle im Computer erzeugen, mit denen sich gezielt bestimmte Mechanismen von Organismen simulieren und am Rechner analysieren lassen. Dieses Forschungsfeld wird Systembiologie genannt und soll langfristig langwierige Experimente sowie teure Tests ergänzen oder womöglich ersetzen. Um der Systembiologie auf europäischer Ebene mehr Gewicht zu verschaffen und die verschiedenen nationalen Förderstrategien zu koordinieren, haben sich unter der Koordination von Deutschland zwölf Länder zum Netzwerk „ERASysbio“ zusammengeschlossen. Im April 2007 ist die erste grenzüberschreitende Forschungsinitiative gestartet, die sich mit einzelligen Mikroorganismen beschäftigt.
Die Systembiologie ist noch ein relativ junger, interdisziplinärer Forschungszweig, könnte langfristig jedoch in vielen Bereichen Anwendung finden. Gemeinsam mit Mathematikern und Informatikern wollen Biologen und Mediziner virtuelle Modelle am Rechner konzipieren, um komplexe biologische Vorgänge in Zellen oder ganzen Organismen nachzustellen und vorherzusagen. Ziel ist es, langwierige und kostspielige Experimente zu ergänzen oder langfristig sogar zu ersetzen. In der biomedizinischen Forschung könnte dies bei toxikologischen Untersuchungen bei der Bewertung von neuen Medikamenten Anwendung finden. In der industriellen Biotechnologie erhoffen sich Experten von der Systembiologie, dass sich mit virtuellen Modellen die Suche nach effizienteren und kostensparenden Produktionsverfahren erleichtern lässt. Noch steht die Systembiologie jedoch ganz am Anfang: Allein um Modelle einfacher Lebewesen wie Bakterien zu erstellen, bedarf es riesiger Mengen an Daten, die zunächst in Experimenten gewonnen und anschließend in mathematische Formeln übersetzt werden müssen.
Um dieses Forschungsgebiet auf europäische Ebene gezielt voranzubringen und nationale Anstrengungen besser aufeinander abzustimmen, haben sich im Jahr 2005 zwölf Länder zu einem ERA-NET zusammengeschlossen. Das ERA-NET Schema ist ein von der Europäischen Kommission eingeführtes Förderinstrument, um die finanzielle Unterstützung von europäischen Forschern zu harmonisieren und Doppelarbeiten in einzelnen Ländern zu verhindern. Das Netzwerk „ERASysbio“ wird von Deutschland aus koordiniert, über den vom Bundesministerium für Bildung und Forschung (BMBF) beauftragten Projektträger Jülich, und will die nationale Förderagenturen und Ministerien unter einem Dach vereinen. Neben Deutschland sind Großbritannien, Österreich, Belgien, Finnland, Frankreich, Israel, Niederlande, Norwegen, Slowenien und Italien vertreten. Bis zum Jahr 2008 wollen sich die beteiligten Partner auf eine gemeinsame Forschungsagenda einigen und Schwerpunkte festlegen, die langfristig finanziell unterstützt werden sollen.
Mit Mikroorganismen starten: SysMo als Pilotprojekt
Als Pilotprojekt ist dabei die Initiative „SysMo – Systembiologie an Mikroorganismen“ ins Leben gerufen worden, die auf so großes Interesse traf, dass bereits Ende 2005 eine erste gemeinsame Ausschreibung erfolgte. Elf Forschergruppen aus Deutschland, Großbritannien, den Niederlanden, Norwegen, Österreich und Spanien erhalten seit April 2007 für die kommenden drei Jahre insgesamt 28 Millionen Euro, um systembiologische Ansätze zur Erforschung von Mikroorganismen voranzutreiben. Das meiste Geld wird hierbei von deutscher und britischer Seite investiert, die jeweils 11 Millionen Euro bereitstellen.
Wegen ihrer geringen Komplexität in Vergleich zu mehrzelligen Organismen und ihrer medizinischen und ökonomischen Relevanz stehen dabei einzellige Mikroorganismen als Untersuchungsobjekt im Mittelpunkt der SysMO-Initiative. Drei der insgesamt elf Projekte werden von deutschen Wissenschaftlern koordiniert. So betreut beispielsweise Michael Hecker, Leiter des Instituts für Mikrobiologie und Molekularbiologie von der Universität Greifswald , das Projekt BaCell-SysMO, an dem insgesamt 17 Partner aus fünf Länder beteiligt sind. Die Wissenschaftler beschäftigen sich dabei mit einem der wichtigsten Mikroorganismen der industriellen Biotechnologie, dem Bakterium Bacillus subtilis, dessen Genomsequenz bereits vollständig entschlüsselt wurde. Anhand von mathematischen Modellierungen wollen die Forscher ein zusammenhängendes Bild der Einzeller zu gewinnen: Vom Genom bis hin zum Stoffwechsel. Damit soll die Suche nach entscheidenden Faktoren bei bestimmten Wachstumsphasen des Bakteriums erleichtert werden.
Mit Computermodellen Bakterien auf der Spur
Ein anderes SysMo-Projekt wird wiederum von Peter Dürre, Direktor des Instituts für mikrobiologie und Biotechnologie der Universität Ulm, koordiniert. (Mehr Informationen zu Peter Dürre erhalten Sie in unserer Rubrik Forscherprofile) Zusammen mit dänischen und britischen Kollegen wollen die deutschen Wissenschaftler um Dürre per Computersimulation ermittteln, wie das Bakterium Clostridium acetobutylicum auf Veränderungen der Umwelt reagiert. Diese Bakterien stellen aus Zucker den Alkohol Butanol her, der angesichts knapper Rohstoffe als Biosprit von großem Interesse ist. Mathematische Simulationen könnten die Suche nach den optimalen Produktionsbedingungen mit den Bakterien erleichtern, so die Hoffnung der Wissenschaftler.
Im dritten von Deutschland aus koordinierten Projekt (PSYSMO) steht das Bakterium Pseudomonas putida. Diese Mikroorganismen sind wichtig für die mikrobiologische Sanierung von verschmutzten Gewässern und anderen Umweltverschmutzungen. Das Team von britischen, spanischen und deutschen Forschern um Vitor Martins dos Santos vom Braunschweiger Helmholtz Zentrum für Infektionsforschung hat sich dabei zum Ziel gesetzt, mithilfe der Systembiologie biotechnologisch eingeleitete Stressmerkmale bei diesen Bakterien zu analysieren.